王震波研究組揭示胚胎期生殖細胞H3K9me2的重建參與雌性減數分裂前期進程
在哺乳動物發育過程中,成熟單倍體配子的形成起始於原始生殖細胞(Primordial Germ Cells,PGCs)的譜係發育。以小鼠為模型的研究表明,PGCs從胚胎期形成,曆經遷移至生殖脊直至完成性別分化的整個過程中,始終維持著高度動態的表觀遺傳重編程狀態。這一特征性現象主要表現為全基因組範圍的DNA去甲基化[1]、H3K9me2組蛋白修飾的顯著減少以及H3K27me3修飾的廣泛獲得[2]。現有證據表明,這種大規模的表觀遺傳重塑可能對維持PGCs的多能性潛能具有關鍵作用[3]。
隨著性別分化完成,雌性生殖細胞在胚胎發育第13.5天(E13.5)開始有序進入減數分裂程序。至出生前,絕大多數雌性生殖細胞發育並停滯在第一次減數分裂前期的雙線期(diplotene stage)。這一複雜的發育進程涉及DNA複製、程序性DNA雙鏈斷裂的形成與修複、同源染色體聯會以及交叉互換等關鍵生物學事件,這些機製共同確保了遺傳物質的穩定傳遞和遺傳多樣性。值得注意的是,在減數分裂前期進展過程中,很可能伴隨著特定的表觀遺傳重編程事件,這些事件可能通過調控減數分裂相關基因的表達網絡來精確協調減數分裂進程。基於上述背景,本研究重點關注以下科學問題:(1)在第一次減數分裂前期,哪些特定的表觀遺傳修飾發生了顯著的重編程變化?(2)這些表觀遺傳修飾如何影響減數分裂關鍵基因的表達調控?
2025年7月12日,必威精装版app西汉姆联 王震波研究員團隊與廣東省第二人民醫院生殖中心團隊合作,在《Nucleic Acids Research》發表了題為"Re-establishment of H3K9me2 eliminates the transcriptional inhibition of ST18 on meiotic genes and orchestrates female germ cell development"的研究論文。該研究首次係統闡明了H3K9me2表觀遺傳修飾在雌性生殖細胞減數分裂進程中的關鍵作用,為理解減數分裂調控機製及女性生殖發育障礙提供了重要理論突破。
研究團隊發現,在雌性生殖細胞發育過程中,H3K9me2修飾的動態重建對減數分裂的順利進行至關重要。這一過程主要依賴於組蛋白甲基轉移酶EHMT1的表達上調,其介導的H3K9me2修飾可有效抑製轉錄抑製因子ST18的表達。在EHMT1缺失小鼠中,H3K9me2重建失敗導致ST18異常激活,進而抑製多個關鍵減數分裂基因(如Stra8、Sycp3、Dmc1等)的轉錄,最終引發減數分裂前期阻滯及生殖細胞凋亡。該研究揭示了H3K9me2(EHMT1)-ST18-Meiotic genes調控軸在減數分裂基因表達中的重要作用,為深入理解女性生殖細胞發育障礙的分子機製提供了新的研究方向,並為相關生殖疾病的臨床幹預策略提供了潛在靶點。
該研究首先通過免疫熒光染色技術係統分析了雌性生殖細胞在不同發育階段(E11.5有絲分裂期、E13.5有絲-減數分裂轉換期、E15.5減數分裂期)的組蛋白修飾動態變化,發現H3K9me2修飾在減數分裂進程中呈現顯著重建和持續累積的趨勢。進一步利用Cut&Tag-Seq技術對H3K9me2在全基因組的分布進行精確分析,證實其信號密度在減數分裂過程中逐步增強,提示該修飾可能參與調控減數分裂基因表達和減數分裂進程。為探究H3K9me2重建的分子機製,研究團隊構建了生殖細胞EHMT1條件性敲除小鼠模型。結果顯示,EHMT1缺失導致雌性小鼠不育,其生殖細胞因減數分裂阻滯而大量凋亡。深入分析發現,EHMT1缺失小鼠的生殖細胞存在DNA雙鏈斷裂修複缺陷、轉錄組紊亂,且多個減數分裂關鍵基因(如Dmc1、Spata22、Meiob、Sycp1、Scye3、Msh4、Msh5、Mei1等)表達顯著下調。同時,H3K9me2修飾的重建完全受阻。結合Cut&Tag-Seq與轉錄組聯合分析,研究人員鑒定出一組在EHMT1缺失條件下異常上調的轉錄抑製因子,包括ST18、ZNF462、KIF12和ETV6。通過雙熒光素酶報告基因實驗,研究團隊進一步證實ST18可直接結合並抑製部分減數分裂基因的轉錄,而H3K9me2的重建可有效解除ST18的抑製作用,從而確保減數分裂程序的正常進行。
必威精装版app西汉姆联 王震波研究員為該研究的通訊作者;必威精装版app西汉姆联 博士生趙丙旺、已畢業碩士張頤娜和廣東省第二人民醫院生殖中心的孟鐵剛研究員為共同第一作者;必威精装版app西汉姆联 的博士生徐源鴻、魯宜珂、孫思敏、郭佳妮和楊雪梅對本研究也做出了重要貢獻。該研究得到了國家重點研發計劃(2022YFA0806302)、國家自然科學基金(82171646)和北京市自然科學基金(Z240020)的資助。感謝器官再生與智造全國重點實驗室提供的技術平台與資源保障。
原文鏈接:https://academic.oup.com/nar/article/53/13/gkaf657/8198050#525552809
[1] Zeng Y,Chen TP. DNA methylation reprogramming during mammalian development. Genes Dev. 2019;10:257.
[2] Seki Y,Hayashi K,Itoh K et al..Extensive and orderly reprogramming of genome-wide chromatin modifications associated with specification and early development of germ cells in mice. Dev Biol. 2005;278:440–58.10.1016/j.ydbio.2004.11.025.
[3] Seki Y,Yamaji M,Yabuta Y et al..Cellular dynamics associated with the genome-wide epigenetic reprogramming in migrating primordial germ cells in mice. Development. 2007;134:2627–38.10.1242/dev.005611.
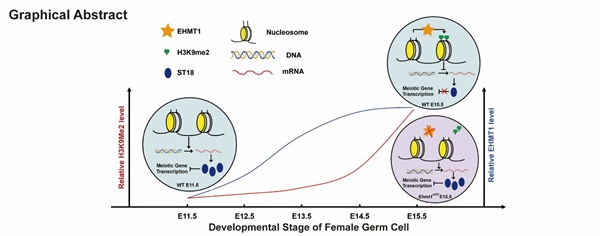
圖1:本研究的圖片摘要
該研究構建了首個結核杆菌感染後肺組織的高精度細胞分子網絡,並運用多維度分析策略係統闡明:細胞衰老與炎症是結核感染後肺損傷的關鍵病理特征,而內皮細胞衰老及血管炎症則是這一過程中的核心事件。進一步,研...

隨著全球氣候偏離曆史常態,物種越來越頻繁的暴露於超出其生理耐受範圍的條件下,這迫使物種需要尋找適宜棲息地或適應變化的環境以避免種群崩潰。因此,理解並量化物種的局部適應性以及氣候變化驅動的脆弱性至關...

在自然界中,生物之間的相互作用是複雜而多樣的,信息交流涉及物理、化學和生物等多個層麵。昆蟲信息素(Insect Pheromone),作為昆蟲體內各種腺體或細胞產生並分泌到體外的微量化學物質,是昆蟲種內和種間通訊...

